科研人员建立高灵敏RNA结合位点检测技术
文章导读
当你在设计gRNA试图精准编辑某个致病RNA时,是否想过那些“脱靶”结合的Cas13蛋白,正在悄悄干扰其他基因的表达?我们用uSpyCLIP技术扫描了两种最常用的Cas13b和Cas13d,发现它们的脱靶行为远比想象中频繁——有些甚至不依赖gRNA就能结合RNA。更关键的是,这些被忽略的结合位点,正在真实改变细胞内mRNA和蛋白水平,可能引发不可预知的毒性反应。这项新技术能在仅1000个细胞中绘制高精度结合图谱,还让检测周期缩短到两天。但问题来了:你现在的RNA编辑方案,真的能排除这些“隐形干扰”吗?
— 内容由好学术AI分析文章内容生成,仅供参考。
近日,中国科学院分子细胞科学卓越创新中心团队等,开发了检测RNA结合蛋白(RBP)在RNA上结合位点的高灵敏、高信噪比深度测序方法uSpyCLIP,并运用这一技术揭示了两种目前应用最为广泛的Cas13核酸酶——Prevotella sp. P5-125 (Psp)Cas13b和Ruminococcus flavefaciens XPD3002 (Rfx)Cas13d的gRNA依赖性以及gRNA非依赖性脱靶结合位点的特征,为未来RNA编辑、检测和治疗应用中Cas13和gRNA的优化设计提供了指导。
该技术通过最小化RBP融合标签设计,降低了对RBP活性的干扰,在识别RBP结合位点时具有高灵敏性和特异性,可以在相同测序深度下检测到更多的结合位点,并支持仅使用1000个细胞完成RBP结合位点图谱测定。此外,uSpyCLIP技术依托磁珠进行操作,便于实现自动化、减少人工投入,且整个流程仅需两天。
研究人员运用uSpyCLIP技术,绘制出dPspCas13b-gRNA和dRfxCas13d-gRNA复合物在转录组中的结合位点分布图谱。结果显示,dCas13的结合行为比先前预想的更为广泛。研究同时对两种dCas13-gRNA复合物的脱靶结合行为进行表征和验证,证实dCas13蛋白的gRNA非依赖性脱靶位点,具有独特的RNA识别位点结构和序列特征。对gRNA依赖性脱靶位点的分析显示,gRNA的DR远端区和中部区域在决定结合特异性中具有关键作用。研究还发现,以上部分脱靶事件导致非靶标基因的mRNA和/或蛋白质水平基因表达发生变化。这表明,基于dCas13或dCas13—效应子融合蛋白的应用,如转录后调控、RNA成像和RNA编辑,可能因脱靶结合而产生复杂的毒副作用。
这一研究为检测Cas13的脱靶结合位点提供了新的技术手段与研究策略,并深化了关于Cas13系统的认知,为特异性gRNA的合理设计以及Cas蛋白的工程改良提供了理论支撑。
相关研究成果在线发表在《核酸研究》(Nucleic Acids Research)上。研究工作得到得到国家自然科学基金委员会、科学技术部、中国科学院的支持。
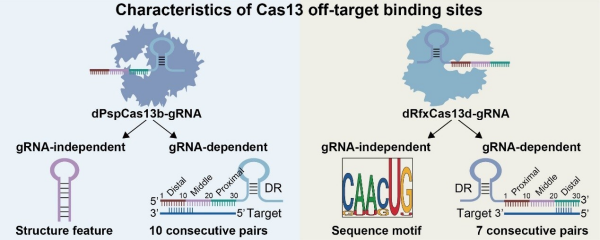
dPspCas13b-gRNA和dRfxCas13d-gRNA复合物脱靶结合位点的特征
© 版权声明
本文由分享者转载或发布,内容仅供学习和交流,版权归原文作者所有。如有侵权,请留言联系更正或删除。














看不太懂但感觉很厉害的样子
自动化流程对实验室太重要了,省人工
这个技术能用在临床样本上吗
DR远端区具体指哪段序列?
有同行验证过这个方法的重复性吗?
Cas13的应用范围比想象中广啊
gRNA非依赖性脱靶这个点挺让人担心的
之前做CLIP实验细胞用量至少十万级,1000个细胞太友好了
两天就能出结果?这效率可以啊
这技术听起来真牛,期待能用上。