文章导读
你还在用传统实验方法逐个筛选蛋白质修饰位点?耗时数月,成本动辄上百万。我们发现,上海交大陈洛南团队的AI新框架,能将预测准确率提升到前所未有的水平——它不只看氨基酸序列,更把蛋白的三维结构“动态折叠”纳入计算。当大多数研究还停留在序列模型时,他们用图神经网络锁定了关键空间接触点。实测中,仅靠算法预测出的两个赖氨酸位点,经分子模拟后证实可直接削弱抗体结合力。这意味着什么?未来药物设计可能不再依赖海量试错,而是由AI先圈出“最值得动手”的靶点。但问题来了:如果AI能提前告诉你哪个位点修饰最有效,你还愿意花大价钱做盲筛吗?
— 内容由好学术AI分析文章内容生成,仅供参考。
2026年2月,上海交通大学数学科学学院陈洛南教授研究团队及合作者在美国科学院院刊PNAS杂志发表了题为“Mining Lysine Post-Translational Modification Site by Integrating Protein Language Model Representations with Structural Context”的研究论文。陈洛南教授、Arieh Warshel教授、白晨博士为论文共同通讯作者,罗梦奇助理教授为第一作者。团队为蛋白质的赖氨酸翻译后修饰位点精准预测开发了一个整合序列与结构信息的AI框架,可有效发掘蛋白质的PTM(Post-Translational Modification)位点,为蛋白质调控研究及制药应用提供支持。

团队构建的预测模型创新性地融合了蛋白质语言模型与图神经网络,同步捕获修饰位点的序列上下文与三维空间结构信息。该模型通过ESM-2提取序列特征,结合基于原子坐标构建的局部接触图进行图卷积处理,最终经多层感知机整合实现高精度预测。

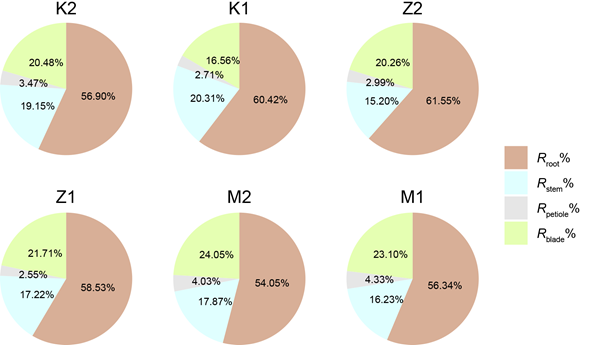
团队成功预测了hCLEC12A蛋白的潜在修饰位点(K174与K181),并构建了5种修饰体系进行分子动力学模拟。结果显示,与未修饰体系相比,单一位点修饰体系(如K181乙酰化)及双修饰体系(如K174巴豆酰化与K181乙酰化)均显著削弱了hCLEC12A与抗体50C1的结合,证实了关键赖氨酸的翻译后修饰可通过干扰界面残基间的相互作用显著降低蛋白与抗体的结合亲和力。

该研究提出的深度学习通用框架,成功揭示了修饰位点调控蛋白-抗体结合的具体机制,为蛋白位点精准预测提供了新范式,也为靶向修饰的疾病干预策略提供了理论依据。该框架的模块化设计可扩展至其他残基水平功能注释任务,推动了计算生物学方法的通用化发展。
论文链接:https://doi.org/10.1073/pnas.2529141123
作者: 数学科学学院 供稿单位: 数学科学学院
© 版权声明
本文由分享者转载或发布,内容仅供学习和交流,版权归原文作者所有。如有侵权,请留言联系更正或删除。


















K174和K181这两个位点是怎么确定的?
纯路人,这标题看得我头大
之前做蛋白结构预测也踩过坑,这个框架挺有意思
这种研究对药物开发帮助大吗?
看不懂,但感觉很厉害的样子